单细胞分析助手
端到端分析 scRNA-seq 数据——质控、聚类、注释、轨迹——无需管理管线。
工作流
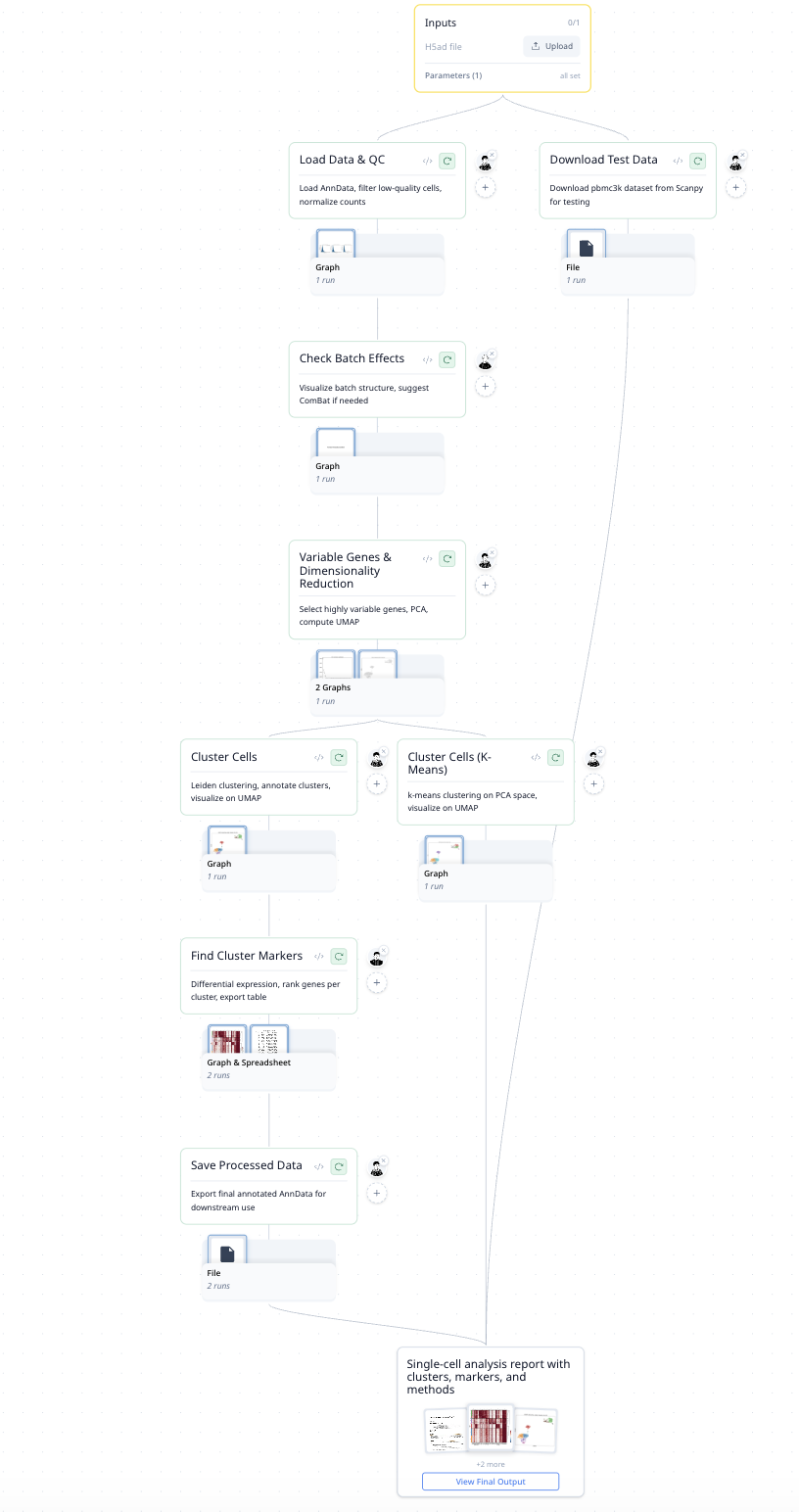
每个步骤都会生成一张图——质控小提琴图、UMAP 嵌入、标记基因热图——让您始终了解发生了什么以及为什么。
| 步骤 | 功能说明 |
|---|---|
| 数据导入 | 加载计数矩阵和细胞元数据 |
| 质量控制 | 按线粒体含量、基因计数、双细胞检测进行细胞过滤 |
| 标准化 | 对数标准化和高变异基因选择 |
| 批次校正 | 仅在检测到批次效应时应用——不需要则跳过 |
| 降维 | PCA 后进行 UMAP 嵌入 |
| 聚类 | Leiden 社区检测,分辨率可调 |
| 细胞类型注释 | 基于标记基因的注释,附带文献引用 |
| 轨迹分析 | 拟时序排序,追踪细胞状态转换 |
如何构建的
"Build a single-cell RNA-seq analysis copilot. Walks through QC, clustering, annotation, differential expression. Use Scanpy. Validate on PBMC 3k as a test case. Every step should produce a figure."
MorphMind 创建了完整的 8 步管线,并在用户运行自己的数据之前,在真实数据集上进行了端到端验证。
为什么比聊天机器人更好
让聊天机器人"分析我的单细胞数据",您会得到一段 Scanpy 脚本。复制粘贴、运行、调试——如果聚类结果看起来不对,从头开始。这就是问题:
- 批次校正不该运行却运行了 — 但您无法判断,因为聊天机器人给了您一个整体脚本。是标准化的问题?是校正的问题?还是分辨率参数的问题?您得加 print 语句并重新运行所有内容。
- 细胞类型注释看起来不对 — 但质控和聚类是正确的。在管线式聊天机器人中,您需要重新运行整个流程。这里您只需用不同的标记基因重新运行注释步骤。
- 您上周告诉它"总是用 Leiden 而不是 Louvain" — 今天它又用了 Louvain。聊天机器人不会记住您的偏好。工作流 Agent 会记住:您偏好的算法、质量阈值、实验室的命名惯例。
| 问题 | 工作流方式 |
|---|---|
| 一个脚本——聚类有误就重新运行所有 | 每步独立——只重新运行聚类 |
| 无法判断错误出在哪里 | 每步生成一张图供检查 |
| 每个会话都忘记您偏好的参数 | 规则持久化:"如果 silhouette < 0.3,重新调整分辨率" |
| 批次校正总是运行 | 条件性:仅在检测到且生物学上不合适时运行 |
示例提示
Upload my 10X count matrix. What cell types are present?
Are there batch effects across my donors? If so, correct them and re-cluster.
Show me the top marker genes for each cluster and annotate the cell types.
Run trajectory analysis — how do cells transition from progenitor to mature state?
常见问题
AI 能做单细胞 RNA-seq 分析吗?
可以。该 Agent 运行完整的基于 Scanpy 的管线——质控、标准化、聚类、注释和轨迹——每个步骤都会产生可视化输出。它可以直接处理 PBMC 3k 等真实数据集。
AI 生成的细胞类型注释可靠吗?
该 Agent 使用基于标记基因的注释并附带文献引用——每个标签都链接到支持证据。独立的验证检查会将注释与已知的细胞类型数据库进行交叉参考,标记不确定的判断。
什么是自动化 scRNA-seq 管线?
一个运行标准单细胞分析工作流(过滤、标准化、聚类、注释)而无需用户编写或调试代码的系统。该 Agent 增加了可引导性:您可以通过对话调整任何步骤的参数,更改会持久保存。